The Plant Genome | 欧山羊草(Ae. biuncialis)连锁图谱揭示了相对于普通小麦的显著基因组重排
欧山羊草( Ae. biuncialis, 2n = 4x = 28, UUMM)具有U和M基因组,是小麦育种中重要的新等位基因来源,可用于提高小麦在极端条件下的产量和品质。然而,由于对野生山羊草属物种的基因组了解不足以及分子工具的缺乏,将有益性状从小麦野生近缘种导入小麦受到限制。
捷克科学院实验植物学研究所的Miroslav Valárik和匈牙利农业研究中心农业研究所的István Molnár团队在The Plant Genome杂志发表题为“A linkage map of Aegilops biuncialis reveals significant genomic rearrangements compared to bread wheat”的论文,揭示了利用来自不同生态地理区域的欧山羊草(Aegilops biuncialis)种质MvGB382和MvGB642杂交产生的224个F2个体,构建了首个异源四倍体欧山羊草的连锁图谱。该图谱包含5663个DArTseq标记,分布在15个连锁群中,对应于13条染色体。由于MvGB382种质中的重排导致缺乏重组,未能构建1M染色体。

主要研究结果介绍
遗传图谱的构建
研究团队利用DArTseq技术对224个F2个体及其亲本(双二歧麦草种质MvGB382和MvGB642)进行基因分型,获得了53,394个标记(包括6273个共显性SNP-DArT和47,121个显性Silico-DArT标记)。经过筛选,最终构建的遗传图谱包含5663个标记,分布在15个连锁群中,总长度为2518 cM,平均标记密度为2.79 cM(表1)。
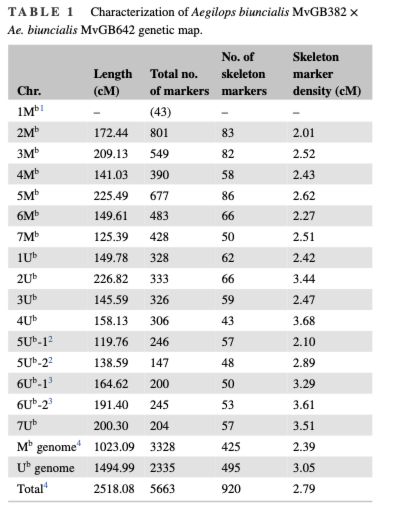 图1
图1染色体结构分析
通过与普通小麦、二倍体U基因组祖先种小伞山羊草(Aegilops umbellulata)和M基因组祖先种卵穗山羊草(Aegilops comosa)的参考基因组进行比较,研究团队评估了欧山羊草亚基因组的共线性和重排情况。结果表明,源自Aegilops comosa的M亚基因组染色体与普通小麦染色体保持高度共线性。相比之下,源自Aegilops umbellulata的U亚基因组表现出不同程度的共线性,其中1U、3U和5U与普通小麦保持基本共线性,而2U、4U、6U和7U表现出显著重排(图2,图3,图4)。
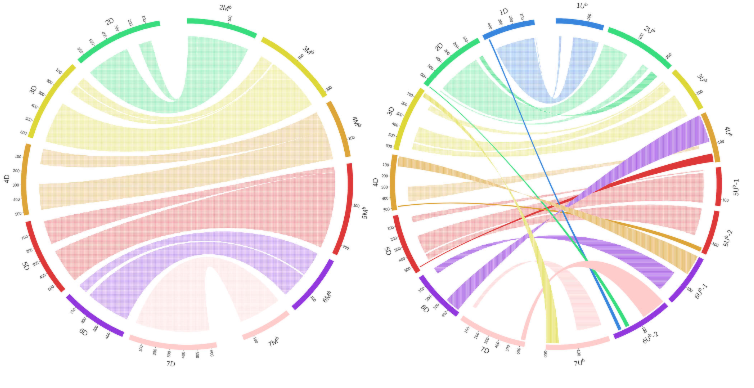 图2
图2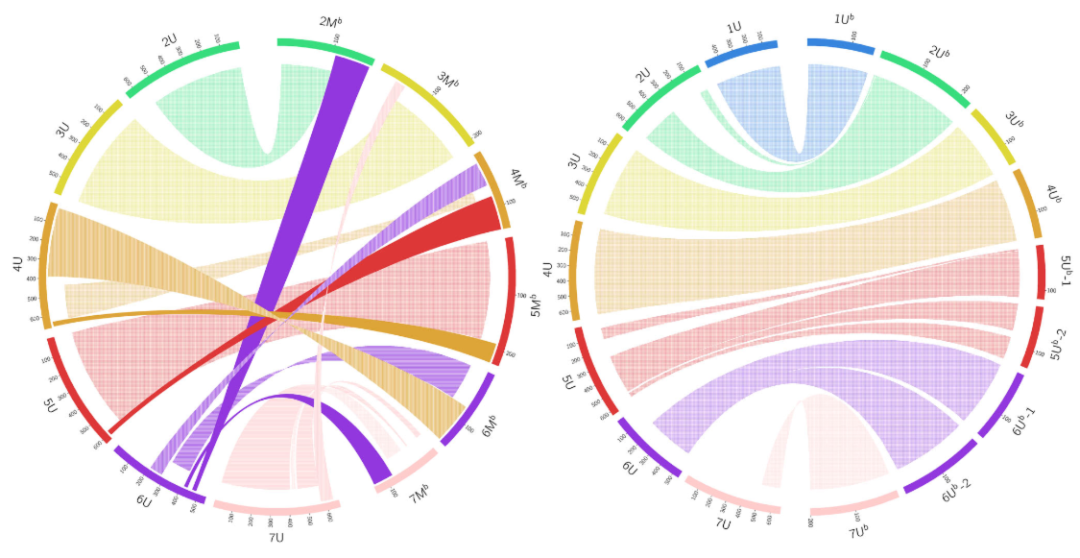 图3
图3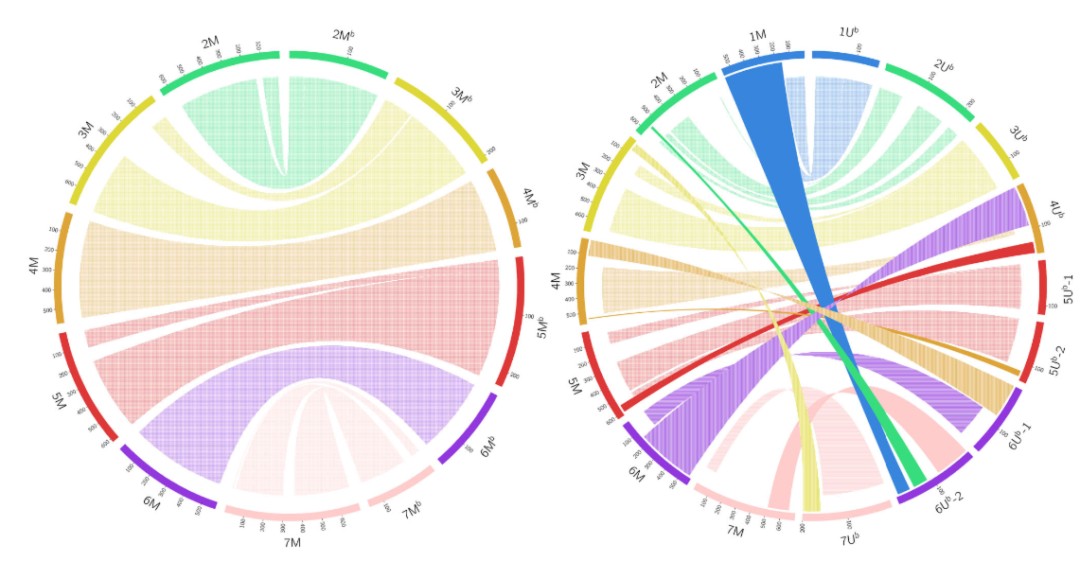 图4
图4育性QTL定位
研究团队对F2群体的育性(每株结实数)进行了表型分析,并在3Mb染色体长臂着丝粒附近鉴定到一个影响育性的数量性状位点(QTL),命名为QFert.ieb-3Mb,解释了23.5%的表型变异(图5,表3)。
 图5
图5全文总结与展望
本研究构建了首个欧山羊草遗传图谱,为小麦育种提供了宝贵的基因资源和分子工具。该图谱揭示了欧山羊草基因组结构,特别是U亚基因组相对于普通小麦的显著重排。这些发现有助于深入了解山羊草属物种的基因组进化,并为将野生山羊草属的有益基因导入小麦提供了重要参考。未来的研究可以利用该图谱进一步定位和克隆与重要农艺性状相关的基因,并开发分子标记辅助选择育种技术,加速小麦遗传改良。
研究团队与资助
该研究由捷克科学院实验植物学研究所的Miroslav Valárik和匈牙利农业研究中心农业研究所的István Molnár团队领导,第一作者为Adam Lampar。该研究得到了匈牙利国家研究、发展和创新办公室、ERDF Programme Johannes Amos Comenius、Marie Curie Fellowship 'AEGILWHEAT'的资助。
DOI链接:https://doi.org/10.1002/tpg2.70009
小麦族多组学网站:http://wheatomics.sdau.edu.cn
投稿、合作等邮箱:shengweima@icloud.com
(转自:小麦研究联盟)
声明:
- 风险提示:以上内容仅来自互联网,文中内容或观点仅作为原作者或者原网站的观点,不代表本站的任何立场,不构成与本站相关的任何投资建议。在作出任何投资决定前,投资者应根据自身情况考虑投资产品相关的风险因素,并于需要时咨询专业投资顾问意见。本站竭力但不能证实上述内容的真实性、准确性和原创性,对此本站不做任何保证和承诺。
- 本站认真尊重知识产权及您的合法权益,如发现本站内容或相关标识侵犯了您的权益,请您与我们联系删除。










推荐文章: